|
|||||
|
|||||||
|
    An initiative of :Stichting Food-Info |
| Food-Info.net> Seguridad alimentarias > Virus Introducción a la clasificación de los virus y la replicaciónAdaptado de http://www.tulane.edu/~dmsander/WWW/224/Classification224.html ClasificaciónLa clasificación hace posibles predicciones sobre detalles de la replicación, patogénesis y transmisión. Esto es particularmente importante cuando se identifica un nuevo virus. Esto también significa que cuando una nueva especie de una familia o género conocido es investigada puede hacerse en el contexto de la información que está disponible por otros miembros de ese grupo. Sin un esquema de la clasificación cada nuevo virus descubierto sería como una caja en blanco. No podría asumirse nada, todo tendría que ser descubierto y redescubierto. Estas razones demuestran que el desarrollo de un esquema de clasificación es importante e inevitable. El esquema de clasificación actual permite situar los virus recientemente descritos en un cuadro con una etiqueta. Incluso en el peor caso se indicaría un marco de trabajo. Por el hecho de que son muy pocos los virus que se están descubriendo que no encajan en el esquema de clasificación, podemos afirmar que la mayoría de los virus que infectan a los animales y los humanos han sido identificados. Por lo tanto, la clasificación es útil. ¿Cómo se clasifican los virus?Clasificación jerárquica de los virus: orden - familia - subfamilia - género - especie cepa/tipo Por el momento la clasificación solo es importante por debajo del nivel de las familias. Todas las familias tienen el sufijo - viridae e.g.
Los miembros de la familia Picornaviridae se trasmiten generalmente vía fecal/oral por medio del aire. El género tiene el sufijo - virus . Por ejemplo en el Picornaviridae hay 5 géneros:
La definición de especie es la misión más difícil de hacer con los virus. Hay un elemento de subjetividad en ello. Considerando el género Lentivirus , es conocido por contener muchas especies distintas incluyendo las siguientes:
Pero hay virus que están entre medias de dos especies descritas. ¿Debería ser una especie diferente o incluirse en una especie conocida? Tales variaciones son un rasgo principalmente de los virus con un genoma de ARN y causa muchas dificultades en la clasificación. Base de la Clasificación Taxonómica.Rasgos como la morfología (tamaño, forma, cápsida o no), propiedades físico-químicas (masa molecular, densidad flotante, pH, térmicas, estabilidad iónica), genoma (RNA, DNA, secuencia segmentada, mapa de restricción, modificaciones etc), macromoléculas (composición y función de la proteína), propiedades antigénicas, biológicas propiedades (hospedador, tropismo de transmisión etc) son todos considerados. La clasificación BaltimoreLa estrategia de replicación de los virus depende de la naturaleza de su genoma. Los virus pueden ser clasificados en siete grupos (arbitrarios) : 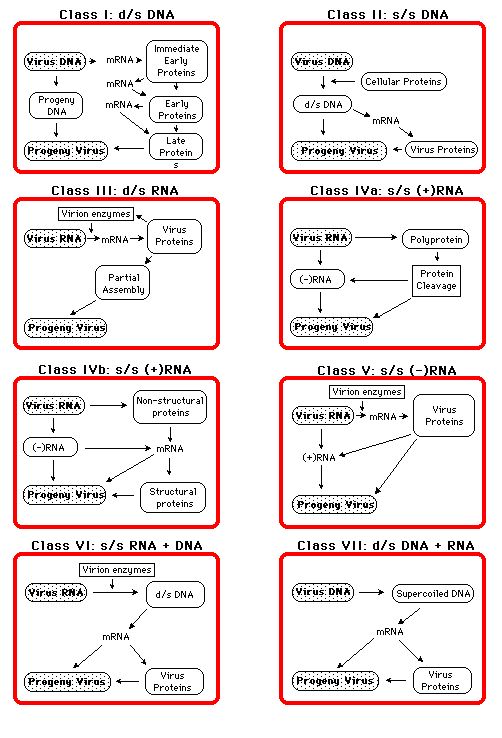 I: Double-stranded (bicatenario) ADN (Adenoviruses; Herpesviruses; Poxviruses, etc) ReplicaciónPara que un virus se multiplique, obviamente debe infectar una célula. Los virus normalmente tienen un rango de hospedadores restringido por ejemplo células animales o vegetales. Todos deben hacer proteínas con 3 series de funciones.- asegura la replicación del genoma envuelve el genoma en el virus altera el metabolismo de la célula infectada con lo que los virus son fabricados. 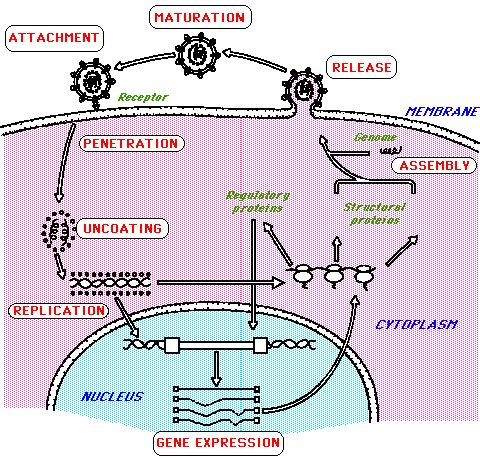 Esto muestra realmente la replicación de un retrovirus, HIV-1 pero las etapas principales son comunes para todos los virus aunque obviamente varían detalles precisos. Fase de iniciación:
El material genético del virus se introduce en la célula, a menudo acompañado por cofactores proteínicos esenciales. Fase de replicación:
El tamaño del genoma, la composición y la organización de los virus muestra una tremenda diversidad (mirar clasificación Baltimore).En unos pocos casos son enzimas celulares que replican el genoma del virus, asistidas por as proteínas virales e.g parvovirus. En la mayoría de los casos lo opuesto es verdad, Las proteínas virales son responsables de la replicación del genoma aunque utilizan proteínas celulares para ayudarse. Fase de liberación:
En todos los casos son proteínas virales las responsables de esta fase tercera y final aunque las proteínas del hospedador y otros factores pueden todavía asociarse con el virus. El ratio particular/infectividad en picornavirus es como poco 0.1% i.e. solo 1 de 1000 partículas son infecciosas. N virus puede ser defectuoso por innumerables razones lo que hace difícil el estudio de la replicación. Más lectura sobre virus: http://www.virology.net/ |
|
| ||||
| Food-Info.net is an initiative of Stichting Food-Info, The Netherlands | 
| |||||||